Single-cell transcriptomics of 20 mouse organs creates a Tabula Muris¶
作者 · Tabula Muris Consortium, 期刊 · Nature, 年份 · 2018, DOI · https://doi.org/10.1038/s41586-018-0590-4
一句话:Tabula Muris 用跨器官单细胞图谱证明,细胞类型既有核心身份,也有被组织环境塑造的局部状态。
1. 背景与前问¶
单细胞技术成熟后,领域马上遇到新问题:每篇论文都给出一批 cluster,但缺少跨组织、跨实验可查询的参考坐标。免疫细胞、内皮细胞、成纤维细胞在不同器官是否相同?一个 marker 在不同组织是否可靠?这些问题需要 atlas,而不是单个处理组实验。
2. 核心问题¶
核心问题一句话:能否为小鼠多个器官建立统一的细胞类型参考,并比较同类细胞在不同组织中的状态差异?
这是一篇资源型论文,但不是简单“测很多细胞”。它的真正价值是把 cell type 变成跨器官可比的分子对象。
3. 实验设计的关键决策¶
研究覆盖 20 个器官,并使用 droplet 与 FACS/plate-based 两条技术路线。droplet 提供通量,FACS/plate 提供更高基因检出和 index sorting 信息。这个双平台设计能部分区分技术偏差和真实生物差异。
样本设计控制了年龄和性别,并尽量从同一批动物取多个器官。这个取舍降低了个体差异,但也意味着 atlas 主要代表特定年龄和健康状态的小鼠。
4. 数据生成与处理¶
核心数据结构是 cell-by-gene matrix。流程包括 QC、归一化、降维、聚类、marker gene identification、cell ontology 标注和跨器官比较。
flowchart LR
Organs[20 organs] --> Cells[单细胞悬液]
Cells --> Droplet[droplet high-throughput]
Cells --> FACS[FACS plate deep profiling]
Droplet --> Matrix[cell×gene]
FACS --> Matrix
Matrix --> Annot[marker + ontology annotation]
Annot --> Compare[跨器官同类细胞比较]统计上,聚类只给 expression similarity;注释需要 marker gene 组合、已知组织学和 cell ontology。
5. 关键 Figure 拆解¶
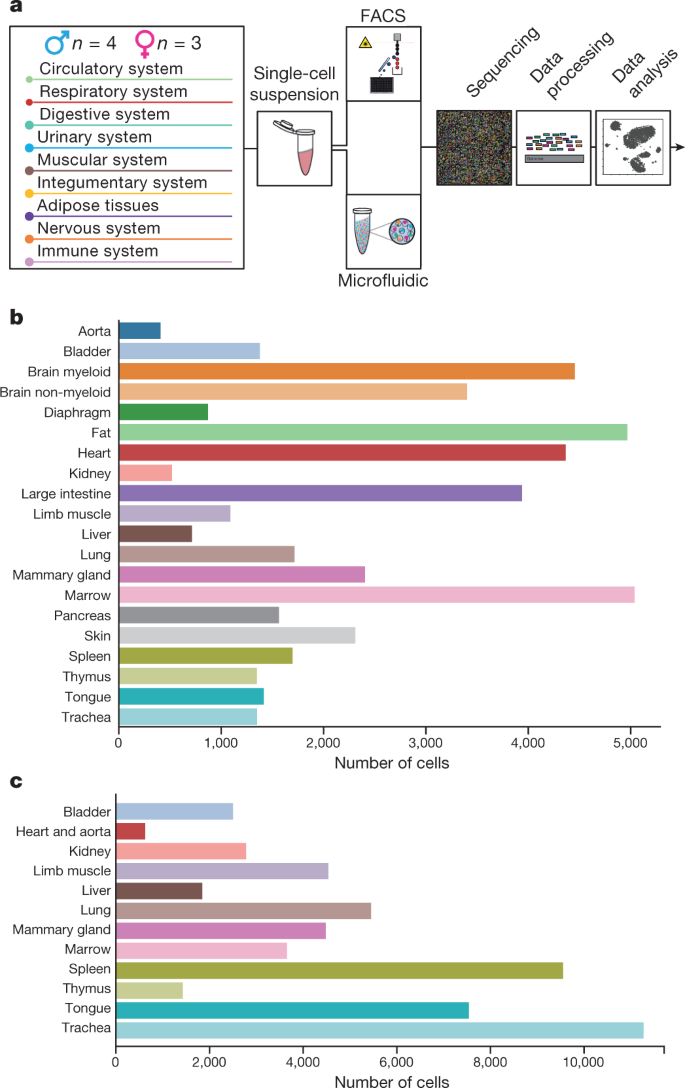
Figure 1:全项目设计和细胞图谱¶
这张图说明样本、器官、平台和总体细胞数。它在统计上定义了 atlas 的覆盖范围。生物学声明是:多个器官中的主要细胞类型可以被系统 catalog。
边界:atlas 覆盖不是无限。脆弱细胞、低丰度细胞和解离困难组织可能被低估。
Figure 2/3:细胞类型注释¶
这些图展示 marker genes 和 cluster annotation。支撑细胞命名的不是 UMAP 坐标,而是 marker 组合与已知细胞生物学一致。例如 T cells、B cells、endothelial cells、epithelial cells 都要靠多基因证据。
Figure 4/5:跨器官比较¶
这些图的关键是:同一大类细胞在不同器官共享核心身份,但也保留器官特异表达。生物学声明是组织微环境塑造 cell state。
6. 结论的强度边界¶
强支持:健康成年小鼠多器官主要细胞类型可由 scRNA-seq 系统编目;同类细胞存在跨器官状态差异;双平台数据能互补。
边界:atlas 不等于所有细胞类型本体论;单细胞悬液丢失空间和细胞互作;解离诱导应激和细胞损失会影响比例。把 Tabula Muris 直接当任何疾病或发育阶段参考都要谨慎。
7. 如果今天重做¶
今天会加入 snRNA-seq 处理难解离组织,加入空间转录组定位细胞类型,加入 CITE-seq 或空间蛋白校准 marker,并在统计上用 donor-level pseudobulk 重新评估跨器官差异。对植物 atlas,应从根尖、叶片、花器官等空间结构出发,避免只把 protoplast cluster 命名成“细胞类型”。
8. 我学到了什么¶
(Peter 填)
横向连接¶
- [[04-scRNAseq/cell-type-annotation-paradigms]]
- [[04-scRNAseq/pseudoreplication-pseudobulk]]
- [[06-spatial/scrnaseq-spatial-projection]]
- [[05-snRNAseq/snrna-vs-scrna-molecular]]
参考¶
- Tabula Muris Consortium (2018), Nature, DOI: https://doi.org/10.1038/s41586-018-0590-4
- Han et al. (2018), Cell — Mouse Cell Atlas
- Schaum et al. (2018), Nature — tissue ageing single-cell atlas